EpiG : Epigénomique fonctionnelle
La plateforme Epigénomique Fonctionnelle a pour objectifs d’assurer la mise à disposition d’équipements et de former le personnel à leur utilisation.
Elle propose des prestations de services permettant l’analyse de l’épigénome et participe aux développement de nouvelles techniques en fonction des évolutions du domaine.
La plateforme Epigénomique Fonctionnelle est ouverte à la communauté scientifique académique et industrielle.
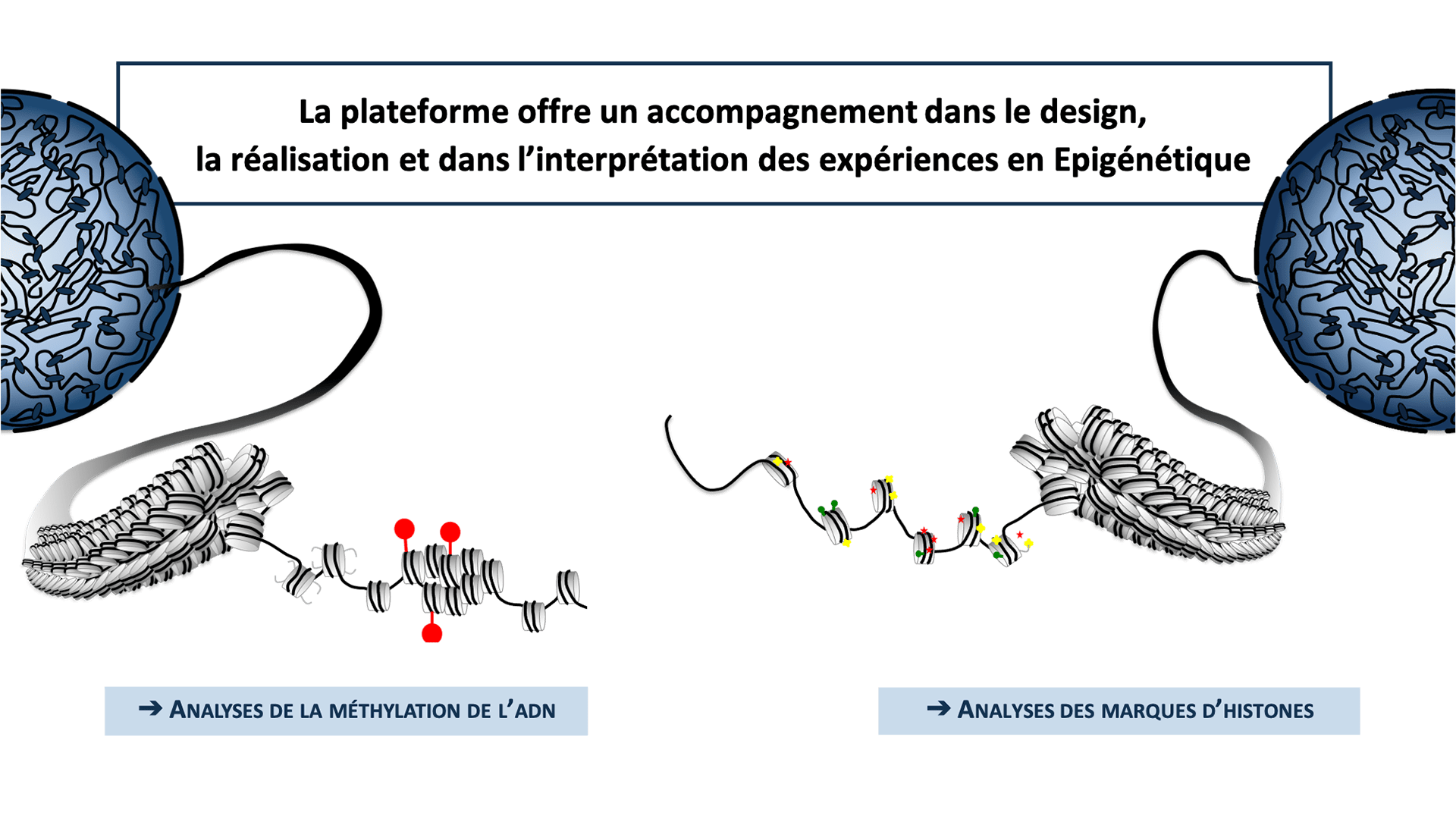
Schéma des expertises de la plateforme
La plateforme offre un accompagnement dans le design, la réalisation et dans l’interprétation des expériences en Epigénétique.
© Laure Ferry
Expertises
La plateforme Epigénomique Fonctionnelle offre une expertise complète pour l’analyse des marques épigénétiques. Elle évalue la faisabilité des projets déposés et propose la méthode la plus adaptée pour leur aboutissement.
Méthylation de l’ADN
- LUMA (LUminometric Methylation Assay)
- MeDIP ou hMeDIP (Methylated ou hydroxyMethylated Immunoprecipitation Assay)
- Bisulfite pyroséquençage
Marques post-tranductionnelles des Histones
- Cut & Run
- ChIP
Soumettre un projet
Vous pouvez nous contacter pour que nous puissions répondre à vos questions et discuter ensemble de votre projet.
Vous devez remplir la fiche de demande de projet et l’envoyer à l’adresse suivante : parisepigenetics.pf@gmail.com
Développements
La plateforme Epigénomique Fonctionnelle s’implique dans le développement de nouvelles techniques d’analyse de l’Epigénome :
- Automatisation Cut & Run
- Cut & Tag
- Enzymatic Methyl-seq ( EM-seq)
- Nanopore
Analyses épigénétiques proposées
Les prestations de service disponibles pour l’analyse de la méthylation de l’ADN et des marques d’histones.
Équipements
Les équipements disponibles sur la plateforme Epigénomique Fonctionnelle.
Membres
Responsable scientifique : Pierre-Antoine Defossez
Responsable technique : Laure Ferry
Comité de Pilotage :
Publications
- Planques A, Pierre K, Ferry L, Grunau C, Gazave E, Vervoort M. DNA methylation atlas and machinery in the developing and regenerating annelid Platynereis dumerilii. BMC Biology, Vol 19, Iss 1, Pp 1-26, 2021. DOI: 10.1186/s12915-021-01074-5
- Marchal C, de Dieuleveult M, Saint-Ruf C, Guinot N, Ferry L, Olalla Saad ST, Lazarini M, Defossez PA, Miotto B. Depletion of ZBTB38 potentiates the effects of DNA demethylating agents in cancer cells via CDKN1C mRNA up-regulation. Oncogenesis; Oct 2018, Vol. 7 Issue 10, p1-18, 18p DOI: 10.1038/s41389-018-0092-0
- Velasco G, Grillo G, Touleimat N, Ferry L, Ivkovic I, Ribierre F, Deleuze JF, Chantalat S, Picard C, Francastel C. Comparative methylome analysis of ICF patients identifies heterochromatin loci that require ZBTB24, CDCA7 and HELLS for their methylated state. Human Molecular Genetics, 2018 Jul 15;27(14):2409-2424. DOI: 10.1093/hmg/ddy130.
- Ferry L, Fournier A, Tsusaka T, Adelmant G, Shimazu T, Matano S, Kirsh O, Amouroux R, Dohmae N, Suzuki T, Filion GJ, Deng W, de Dieuleveult M, Fritsch L, Kudithipudi S, Jeltsch A, Leonhardt H, Hajkova P, Marto JA, Arita K, Shinkai Y, Defossez PA. Methylation of DNA Ligase 1 by G9a/GLP Recruits UHRF1 to Replicating DNA and Regulates DNA Methylation. Molecular Cell. August 17, 2017, Vol. 67 Issue 4, p550. DOI: 10.1016/j.molcel.2017.07.012
- Kebir O, Chaumette B, Rivollier F, Miozzo F, Lemieux Perreault LP, Barhdadi A, Provost S, Plaze M, Bourgin J, the ICAAR team, Gaillard R, Mezger V, Dubé M-P , Krebs M-O. Methylomic changes during conversion to psychosis. Molecular Psychiatry (2017) 22, 512-518. DOI: 10.1038/mp.2016.53.
Contact
Vous pouvez nous contacter par mail à l’adresse suivante : parisepigenetics.pf@gmail.com
Plateforme Epigénomique Fonctionnelle
35 rue Hélène Brion
Bâtiment Lamarck B, RB77-81
75013 PARIS
+33(0)1 57 27 89 26
À lire aussi

Séminaire Adam Sateriale – 17 juin 2026
Dr. Adam Sateriale The Francis Crick Institute, London, UK Invité par Jonathan Weitzman et Marisol Giacomini "Intestinal parasites and metabolic mysteries." Le séminaire se tiendra à l’Institut Jacques Monod, salle François Jacob (RB-18B). Bâtiment Buffon, 15 rue...

Séminaire Laurent CHATRE – 10 juin 2026
Dr. Laurent CHATRE STCT, UMR6030 CNRS, Université de Caen Normandie, France Invité par Dr. Dounia DJEGHLOUL "Reframing Epigenetics: Metabolism, Mitochondria, and Redox as Core Regulatory Layers." Le séminaire se tiendra à l’Institut Jacques Monod, salle François Jacob...

Séminaire Michael Rera – 3 juin 2026
Dr. Michael Rera Unité de Biologie Fonctionnelle et Adaptative, Université Paris Cité, France Invité par Dr.Valerie Mezger "Studying ageing as a two-phase process." The hallmarks of aging framework, introduced over a decade ago and cited nearly 20,000 times, became...

Séminaire Anne-Sophie LEBRE – 27 Mai 2026
Pr. Anne-Sophie LEBRE CHU de Reims - Hôpital Robert Debré, France Invité par Pr. Bertrand Cosson "Brain (epi)genome study in CNS rare disorders" Le séminaire se tiendra à l’Institut Jacques Monod, salle François Jacob (RB-18B). Bâtiment Buffon, 15 rue Hélène...
